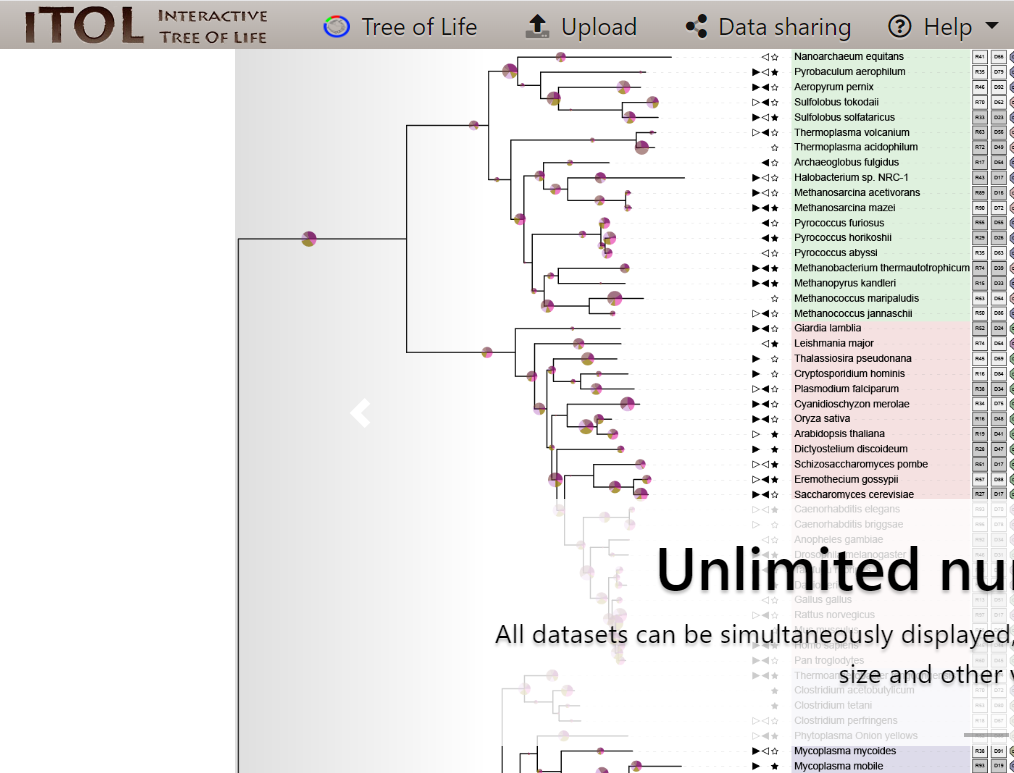
iTOL(Interactive Tree Of Life)是由EMBL(欧洲分子生物学实验室)开发的免费在线交互式系统发育树可视化工具,核心定位是为科研人员提供”从基础展示到深度定制”的进化树可视化解决方案。平台支持多种树文件格式输入,包括Newick、Nexus、PhyloXML等主流格式,可实现进化树的交互式浏览、个性化注释和高质量图像导出,目前已成为生物信息学、进化生物学、微生物学等领域发表论文时绘制进化树的首选工具,累计服务全球数百万科研用户。
iTOL最核心的优势在于高度可定制的交互式可视化能力:基础功能层面,支持进化树的多种布局方式,包括圆形、矩形、斜向、径向等经典布局,以及unrooted(无根树)、cladogram(分支图)等特殊展示形式;用户可通过鼠标拖拽调整分支结构,实时缩放查看细节,点击节点即可显示注释信息。高级定制功能方面,平台提供超过100种注释类型,涵盖颜色条、热图、条形图、饼图、序列比对、基因结构等,可将多组学数据(如基因表达量、代谢物丰度、物种分类信息)与进化树进行关联展示,直观呈现进化关系与功能特征的关联。
在输出与扩展性上,iTOL同样表现出色:支持导出PNG、SVG、PDF等多种格式的高清图像,其中SVG格式为矢量图,可无限放大且不失真,完全满足学术期刊的投稿要求;还支持生成HTML格式的交互式进化树,便于在网页中分享和浏览。针对批量处理需求,iTOL提供命令行工具和API接口,支持自动化生成大量进化树;同时有第三方开发的R包(如itol.toolkit)扩展其功能,可实现批量注释、主题学习和模板复用等高级操作。
iTOL的应用场景覆盖整个生命科学领域:在基因组研究中,可用于展示基因家族的进化关系与功能分化;在微生物研究中,可将OTU树与物种丰度信息结合,直观呈现群落结构;在进化生物学中,可展示物种间的亲缘关系与演化历史;在教学场景中,可用于直观展示生物分类系统。无论是初学者快速查看进化树,还是资深科研人员制作出版级图表,iTOL都能提供高效、专业的解决方案。
数据统计
数据评估
本站囧蒜学术导航提供的iTOL都来源于网络,不保证外部链接的准确性和完整性,同时,对于该外部链接的指向,不由囧蒜学术导航实际控制,在2026年4月11日 上午2:19收录时,该网页上的内容,都属于合规合法,后期网页的内容如出现违规,可以直接联系网站管理员进行删除,囧蒜学术导航不承担任何责任。
相关导航

BioRender
Draw Venn Diagram

Hiplot

Origin

OriginLab

Bioicons

Figdraw